はじめに
前回の記事ではハードマージンSVMの理論について述べました。
今回はそれをふまえてPythonを用いた実装をおこなっていきます。
また、以下のコードはGoogle Colabで動作します。

\begin{align*}
\newcommand{\mat}[1]{\begin{pmatrix} #1 \end{pmatrix}}
\newcommand{\f}[2]{\frac{#1}{#2}}
\newcommand{\pd}[2]{\frac{\partial #1}{\partial #2}}
\newcommand{\d}[2]{\frac{{\rm d}#1}{{\rm d}#2}}
\newcommand{\T}{\mathsf{T}}
\newcommand{\(}{\left(}
\newcommand{\)}{\right)}
\newcommand{\{}{\left\{}
\newcommand{\}}{\right\}}
\newcommand{\[}{\left[}
\newcommand{\]}{\right]}
\newcommand{\dis}{\displaystyle}
\newcommand{\eq}[1]{{\rm Eq}(\ref{#1})}
\newcommand{\n}{\notag\\}
\newcommand{\t}{\ \ \ \ }
\newcommand{\tt}{\t\t\t\t}
\newcommand{\argmax}{\mathop{\rm arg\, max}\limits}
\newcommand{\argmin}{\mathop{\rm arg\, min}\limits}
\def\l<#1>{\left\langle #1 \right\rangle}
\def\us#1_#2{\underset{#2}{#1}}
\def\os#1^#2{\overset{#2}{#1}}
\newcommand{\case}[1]{\{ \begin{array}{ll} #1 \end{array} \right.}
\newcommand{\s}[1]{{\scriptstyle #1}}
\definecolor{myblack}{rgb}{0.27,0.27,0.27}
\definecolor{myred}{rgb}{0.78,0.24,0.18}
\definecolor{myblue}{rgb}{0.0,0.443,0.737}
\definecolor{myyellow}{rgb}{1.0,0.82,0.165}
\definecolor{mygreen}{rgb}{0.24,0.47,0.44}
\newcommand{\c}[2]{\textcolor{#1}{#2}}
\newcommand{\ub}[2]{\underbrace{#1}_{#2}}
\end{align*}
ハードマージンSVMの理論概要
観測した $n$ 個の $p$ 次元データを $X$、$n$ 個のラベル変数の組を $\bm{y}$ として、それぞれ下記と表記します。
\us X_{[n \times p]} = \mat{x_1^{(1)} & x_2^{(1)} & \cdots & x_p^{(1)} \\
x_1^{(2)} & x_2^{(2)} & \cdots & x_p^{(2)} \\
\vdots & \vdots & \ddots & \vdots \\
x_1^{(n)} & x_2^{(2)} & \cdots & x_p^{(n)}}
=
\mat{ – & \bm{x}^{(1)\T} & – \\
– & \bm{x}^{(2)\T} & – \\
& \vdots & \\
– & \bm{x}^{(n)\T} & – \\},
\t
\us \bm{y}_{[n \times 1]} = \mat{y^{(1)} \\ y^{(2)} \\ \vdots \\ y^{(n)}}.
\end{align*}
前回の帰結から、分離超平面を決定するパラメータは次式で計算できるのでした。
\hat{\bm{w}} &= \sum_{\bm{x}^{(i)} \in S} \hat{\alpha}_i y^{(i)} \bm{x}^{(i)}, \\
\hat{b} &= \f{1}{|S|} \sum_{\bm{x}^{(i)} \in S} (y^{(i)} – \hat{\bm{w}}^\T \bm{x}^{(i)}).
\end{align}
(ここで、$S$ はサポートベクトルの集合)
また、$\bm{\alpha} = (\alpha_1, \alpha_2, \dots, \alpha_n)^\T$ はラグランジュの未定乗数の組で、ここでは最急降下法を用いて、その最適解 $\hat{\bm{\alpha}}$ を求めます。
\bm{\alpha}^{[t+1]} = \bm{\alpha}^{[t]} + \eta \pd{\tilde{L}(\bm{\alpha})}{\bm{\alpha}}.
\end{align*}
勾配ベクトル $\pd{\tilde{L}(\bm{\alpha})}{\bm{\alpha}}$ の値は、
\us H_{[n \times n]} \equiv \us \bm{y}_{[n \times 1]} \us \bm{y}^{\T}_{[1 \times n]} \odot \us X_{[n \times p]} \us X^{\T}_{[p \times n]}
\end{align}
を用いて、
\begin{align}
\pd{\tilde{L}(\bm{\alpha})}{\bm{\alpha}} = \bm{1}\, – H \bm{\alpha}.
\end{align}
として計算できました。
ハードマージンSVMをフルスクラッチで実装
上記より、ハードマージンSVMをフルスクラッチで実装します。
import numpy as np
class HardMarginSVM:
"""
Attributes
----------
eta : float
学習率
epoch : int
エポック数
random_state : int
乱数シード
is_trained : bool
学習完了フラグ
num_samples : int
学習データのサンプル数
num_features : int
特徴量の数
w : NDArray[float]
パラメータベクトル: (num_features, )のndarray
b : float
切片パラメータ
alpha : NDArray[float]
未定乗数: (num_samples, )のndarray
Methods
-------
fit -> None
学習データについてパラメータベクトルを適合させる
predict -> NDArray[int]
予測値を返却する
"""
def __init__(self, eta=0.001, epoch=1000, random_state=42):
self.eta = eta
self.epoch = epoch
self.random_state = random_state
self.is_trained = False
def fit(self, X, y):
"""
学習データについてパラメータベクトルを適合させる
Parameters
----------
X : NDArray[NDArray[float]]
学習データ: (num_samples, num_features)の行列
y : NDArray[float]
学習データの教師ラベル: (num_samples)のndarray
"""
self.num_samples = X.shape[0]
self.num_features = X.shape[1]
# パラメータベクトルを0で初期化
self.w = np.zeros(self.num_features)
self.b = 0
# 乱数生成器
rgen = np.random.RandomState(self.random_state)
# 正規乱数を用いてalpha(未定乗数)を初期化
self.alpha = rgen.normal(loc=0.0, scale=0.01, size=self.num_samples)
# 最急降下法を用いて双対問題を解く
for _ in range(self.epoch):
self._cycle(X, y)
# サポートベクトルのindexを取得
indexes_sv = [i for i in range(self.num_samples) if self.alpha[i] != 0]
# w を計算 (式1)
for i in indexes_sv:
self.w += self.alpha[i] * y[i] * X[i]
# b を計算 (式2)
for i in indexes_sv:
self.b += y[i] - (self.w @ X[i])
self.b /= len(indexes_sv)
# 学習完了のフラグを立てる
self.is_trained = True
def predict(self, X):
"""
予測値を返却する
Parameters
----------
X : NDArray[NDArray[float]]
分類したいデータ: (any, num_features)の行列
Returns
-------
result : NDArray[int]
分類結果 -1 or 1: (any, )のndarray
"""
if not self.is_trained:
raise Exception('This model is not trained.')
hyperplane = X @ self.w + self.b
result = np.where(hyperplane > 0, 1, -1)
return result
def _cycle(self, X, y):
"""
勾配降下法の1サイクル
Parameters
----------
X : NDArray[NDArray[float]]
学習データ: (num_samples, num_features)の行列
y : NDArray[float]
学習データの教師ラベル: (num_samples)のndarray
"""
y = y.reshape([-1, 1]) # (num_samples, 1)の行列にreshape
H = (y @ y.T) * (X @ X.T) # (式3)
# 勾配ベクトルを計算
grad = np.ones(self.num_samples) - H @ self.alpha # (式4)
# alpha(未定乗数)の更新
self.alpha += self.eta * grad
# alpha(未定乗数)の各成分はゼロ以上である必要があるので負の成分をゼロにする
self.alpha = np.where(self.alpha < 0, 0, self.alpha)irisデータセットを用いたSVMの動作確認
例として用いるデータはirisデータセットを使用します。 irisデータセットは3種類の品種: Versicolour, Virginica, Setosa の花弁(petal)とガク(sepal)の長さで構成されています。

scikit-learnライブラリを用いてirisデータセットを読み込んでみましょう。
import pandas as pd
from sklearn.datasets import load_iris
iris = load_iris() # irisデータセットの読み込み
df_iris = pd.DataFrame(iris.data, columns=iris.feature_names)
df_iris['class'] = iris.target
df_iris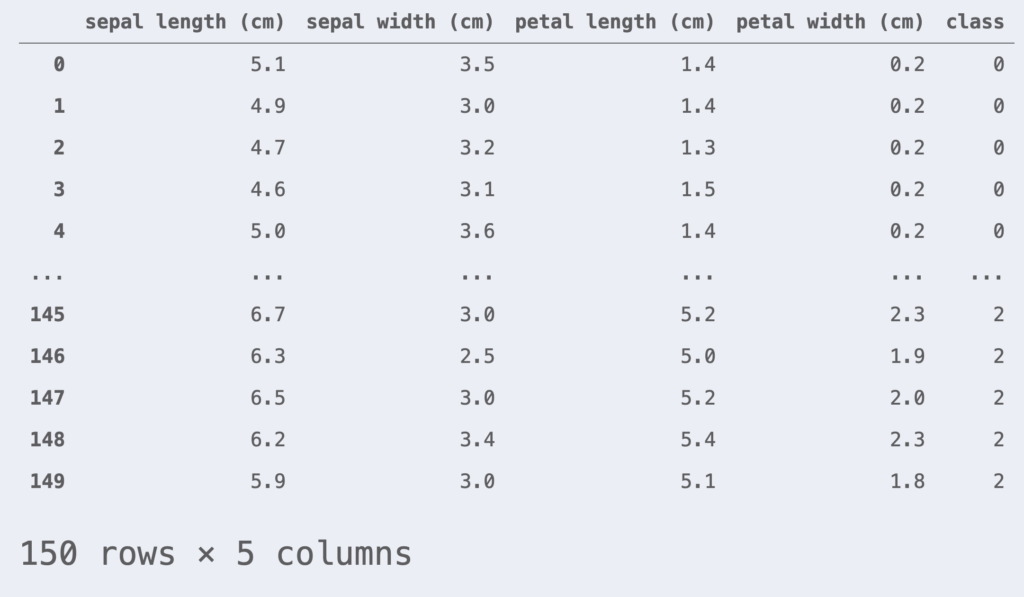
今回はロジスティック回帰の2値分類をおこないます。class = 0, 1 のデータだけに注目します。また、簡単のために特徴量は petal length, petal width の2つとします。
df_iris = df_iris[df_iris['class'] != 2] # class = 0, 1のデータのみを取得
df_iris = df_iris[['petal length (cm)', 'petal width (cm)', 'class']]
X = df_iris.iloc[:, :-1].values
y = df_iris.iloc[:, -1].values
y = np.where(y==0, -1, 1) # class = 0のラベルを-1に変更するまた、データセットの平均値0, 標準偏差1となるように標準化をおこないます。
from sklearn.preprocessing import StandardScaler
# 標準化のインスタンスを生成(平均=0, 標準偏差=1 に変換)
sc = StandardScaler()
X_std = sc.fit_transform(X)モデルの汎化性能を評価するために、データセットを訓練データセットとテストデータセットに分割します。ここでは訓練データ80%, テストデータ20%の割合で分割しました。
from sklearn.model_selection import train_test_split
X_train, X_test, y_train, y_test = train_test_split(X_std, y, test_size=0.2, random_state=42, stratify=y)また、プロットクラスもここで定義しておきます。
# 分類境界のプロットクラスを定義
import matplotlib.pyplot as plt
from matplotlib.colors import ListedColormap
class DecisionPlotter:
def __init__(self, X, y, classifier, test_idx=None):
self.X = X
self.y = y
self.classifier = classifier
self.test_idx = test_idx
self.colors = ['#de3838', '#007bc3', '#ffd12a']
self.markers = ['o', 'x', ',']
self.labels = ['setosa', 'versicolor', 'virginica']
def plot(self):
cmap = ListedColormap(self.colors[:len(np.unique(self.y))])
# グリットポイントの生成
xx1, xx2 = np.meshgrid(
np.arange(self.X[:,0].min()-1, self.X[:,0].max()+1, 0.01),
np.arange(self.X[:,1].min()-1, self.X[:,1].max()+1, 0.01))
# 各meshgridの予測値を求める
Z = self.classifier.predict(np.array([xx1.ravel(), xx2.ravel()]).T)
Z = Z.reshape(xx1.shape)
# 等高線のプロット
plt.contourf(xx1, xx2, Z, alpha=0.2, cmap=cmap)
plt.xlim(xx1.min(), xx1.max())
plt.ylim(xx2.min(), xx2.max())
# classごとにデータ点をプロット
for idx, cl, in enumerate(np.unique(self.y)):
plt.scatter(
x=self.X[self.y==cl, 0], y=self.X[self.y==cl, 1],
alpha=0.8,
c=self.colors[idx],
marker=self.markers[idx],
label=self.labels[idx])
# テストデータの強調
if self.test_idx is not None:
X_test, y_test = self.X[self.test_idx, :], self.y[self.test_idx]
plt.scatter(
X_test[:, 0], X_test[:, 1],
alpha=0.9,
c='None',
edgecolor='gray',
marker='o',
s=100,
label='test set')
plt.legend()それでは、irisデータセットを用いてSVMの動作確認をおこないます。
# svmのパラメータを学習
hard_margin_svm = HardMarginSVM()
hard_margin_svm.fit(X_train, y_train)
# 学習データとテストデータを結合
X_comb = np.vstack((X_train, X_test))
y_comb = np.hstack((y_train, y_test))
# プロット
dp = DecisionPlotter(X=X_comb, y=y_comb, classifier=hard_margin_svm, test_idx=range(len(y_train), len(y_comb)))
dp.plot()
plt.xlabel('petal length [standardized]')
plt.ylabel('petal width [standardized]')
plt.show()このように決定曲線がプロットできました。
scikit-learnを用いたSVMの実装
scikit-learn を用いたSVMの実行は下記のようにできます。
from sklearn import svm
sk_svm = svm.LinearSVC(C=1e10, random_state=42)
sk_svm.fit(X_train, y_train)
# 訓練データとテストデータを結合
X_comb = np.vstack((X_train, X_test))
y_comb = np.hstack((y_train, y_test))
# プロット
dp = DecisionPlotter(X=X_comb, y=y_comb, classifier=sk_svm, test_idx=range(len(y_train), len(y_comb)))
dp.plot()
plt.xlabel('petal length [standardized]')
plt.ylabel('petal width [standardized]')
plt.show()scikit-learnでもこのように決定曲線をプロットすることができました。
以上のコードはこちら▼で試すことができます。

▼ ソフトマージンSVMの実装はこちら







